研究人员已经用广泛使用的方法确定了晶体结构中氢原子的精确位置
从水的物理性质到DNA和蛋白质的生物功能,氢原子对一切都至关重要。然而,在蛋白质的晶体结构中,甚至在小的有机分子中,捕捉它们是很棘手的。现在,研究人员对传统技术进行了改进,使各地的晶体学家都能准确地描绘出氢原子的位置——至少是小分子的位置。1
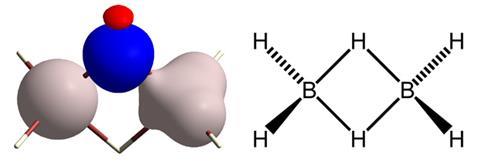
通常只有使用中子衍射才能获得分子氢原子位置的良好图像,而中子衍射只能在极少数设备中以巨大的成本使用。西蒙Grabowsky来自德国不来梅大学的研究人员与来自波兰和澳大利亚的同事一起,使用传统的晶体学数据集,但改进了产生与x射线衍射数据相匹配的结构所需的量子力学模型。格拉博夫斯基解释说:“我们使用了一个数学上更先进的模型(赫什菲尔德原子精化),其中包括键合效应,因此实验数据可以更成功地重建,从而准确地定位氢原子。”
将该方法应用于已知的81个小分子的晶体结构的测试表明,它可以像中子衍射一样精确地确定氢和其他原子之间的键长。这种改进可以用免费软件来完成,根据分子的大小,在普通的个人电脑上需要几个小时到几天的计算时间。
路易Farrugia来自英国格拉斯哥大学的他没有参与这项新工作,他注意到之前一些使用平均质量x射线数据的尝试不太成功,但他承认“这是一个有趣的过程,有了高质量的数据,它肯定会得到接近中子衍射标准的结果”。晶体理事长绪方Hideaki来自德国米
蛋白质中的氢则是一个更大的挑战。它们通常根本不会出现,尽管绪方和他的同事最近在一项研究中发现了氢化酶中的大多数氢,其数据分辨率非常高——这项研究的动机是氢在这种酶中的功能重要性。2
Grabowsky警告说,赫什菲尔德方法不适用于蛋白质,因为即使在晶体中,无序仍然是一个问题。格拉博夫斯基解释说:“在赫什菲尔德原子精化中,我们需要计算待精化分子的量子力学波函数。”“没有办法计算运动粒子或重叠分子的波函数。波函数始终是静态的,并且始终只适用于单个分子或分子组合。因此,蛋白质晶体学家想要知道氢原子的确切键长,目前只能依靠中子衍射。
参考文献
1M Woinska等,科学。睡觉。, 2016,2, e1600192 (DOI:10.1126 / sciadv.1600192)
2绪方,西川和卢比茨,自然, 2015,520, 571 (doi:10.1038 / nature14110)








暂无评论